There are currently three main axes of research in the HMI lab:
- Deciphering the activity and functioning of the Type Three Secretion Apparatus
We previously reported the development of transcriptional reporter of the Type Three Secretion Apparatus (T3SA) in Shigella flexneri (See Figure 1) based on the Green Fluorescent Protein (GFP) as shown in the colorful image on top of this page. Capitalizing on this achievement, we are now working on new assays that will enable delineating the functional mechanism, monitoring in real time the activity and identifying inhibitors of the T3SA.

Figure 1. Scheme of the T3SA of S. flexneri in the inactive (A) and active states (B). IM, bacterial inner membrane; OM, bacterial outer membrane; HPM, host plasma membrane. Picture taken from this review article.
- Adaptation of Microbes to their host
Intracellular pathogens are often treated as homogenous populations, while in fact they are exposed to diverse microenvironments within their host. We are interested to study these adaptive events by isolating bacterial subpopulations and determining their specific transcriptional program.

Figure 2. Microbes adapt to diverse microenvironments within their host. Two bacterial subpopulations [Sub-population (S-P) (-): red; Sub-population (S-P) (+): green] are located in different sites in its host; here, the tissue colonized is the large intestine (A). In the classic approach the transcriptome of the total population is studied to assess the global adaptive process of a microbe within its host. The capacity of isolating the subpopulations bring the prospect of determining the adpative processes taking place in parallel during colonization of different sites within the host (B). Picture adapted from this review article.
- Host-Microbes Protein Interaction Network
Many bacteria inject proteins called effectors inside host cells. We are interested to identify molecular interactions between bacterial effectors and host proteins. To do this, we are developing molecular affinity purification methods that will be used to build an integrated view of host-microbe protein-protein interactions network.
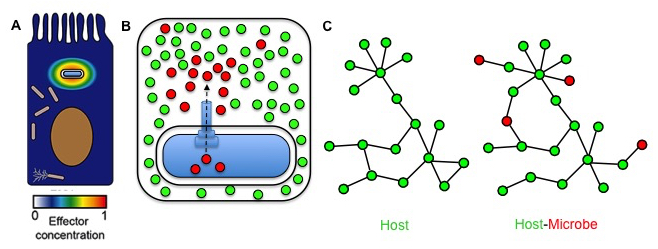
Figure 3. Host-microbe protein-protein interaction network. Many intracellular pathogens such as Shigella inject proteins called effectors in the cytoplasm of host cells using their T3SA. The T3SA is active mostly in bacteria found in vacuolar compartments, thereby forming a gradient of bacterial effectors within the host cell (A). Upon their delivery through the T3SA, effectors (red circles) are released in the host cytoplasm (represented by the space delimited by the outer shape) that obviously contains high amount of host protein (green circles) (B). In normal conditions, proteins form networks that are the basis of cellular functions (e.g. metabolism, signaling pathways etc.). The delivery of effectors perturbs the organization of the host protein-protein interaction networks, which is necessary for the infection process (C). Picture parlty adapted from this review article.
- Décrypter l’activité et le fonctionnement de l’appareil de sécrétion de type III
Nous avons précédemment rapporté le développement de rapporteur transcriptionnel de l’appareil de sécrétion de type trois chez Shigella flexneri (T3SA) reposant sur la protéine fluorescente verte (GFP). Nous travaillons actuellement sur de nouveaux tests qui permettront de délimiter le mécanisme fonctionnel, suivre en temps réel l’activité et identifier des inhibiteurs du T3SA.

Figure 1. Schéma du T3SA de S. flexneri en conformation inactive (A) et active (B). IM, membrane interne de la bactérie; OM, membrane externe de la bactérie; HPM, membrane plasmique de l’hôte. Image tirée de cet article de synthèse de la littérature.
- Adaptation des Microbes à leur hôte
Les pathogènes intracellulaires sont souvent traités comme une population homogène, alors qu’en fait, ils sont exposés à des microenvironnements diverses au sein de leur hôte . Nous voulons étudier ces événements adaptatifs en determinant le programme transcriptionel spécifique des diverses sous-populations bactériennes.

Figure 2. Les microbes s’adaptent à divers micro-environnement dans leur hôte. Deux sous-population bactériennes [sous-population (S-P) (-): rouge; sous-population (S-P) (+): vert] sont localisées dans des sites différents de leur hôte; dans cet exemple, le tissue colonisé est le gros intestin (A). Habituellement, le transcriptome de la population totale est étudié pour obtenir la réponse adaptative globale d’une microbe au sein de son hôte. La capacité d’isoler les sous-populations bactériennes permettraient de déterminer les processus adapatatifs prenant place au même moment durant la colonisation de différents sites dans l’hôte (B). Image adaptée de cet article de synthèse de la littérature.
- Réseau d’interaction protein-protéine hôte-microbe
De nombreuses bactéries injectent des protéines dénommées effecteurs à l’intérieur de leurs cellules hôtes. Nous voulons identifier les interactions moléculaires entre les effecteurs bactériens et les protéines de l’hôte. Pour ce faire, nous développons des méthodes de purification par affinité qui nous permettrons d’obtenir une vision intégrée des réseaux d’interaction protéine-protéine hôte-microbe.
